Genetische Artbestimmung von Gewässerorganismen
Die Einstufung des ökologischen Zustandes von Oberflächengewässern (Flüsse, Seen) basiert auf der Bestimmung der dort lebenden Gewässerorganismen. Für die Untersuchung werden die vier biologischen Qualitätskomponenten Makrozoobenthos, Makrophyten & Phytobenthos, Phytoplankton und Fische betrachtet. Konventionelle Bestimmungsmethoden für die jeweiligen Arten erfolgen über morphologische Merkmale (Aussehen), die oft nicht zweifelsfrei erkennbar sind oder u.U. nur zeitweise ausgebildet werden. Die genetische Identifizierung über DNA-Analysen – das sogenannte DNA-Barcoding – ist hingegen die genaueste Methode für eine exakte und sichere Artbestimmung.
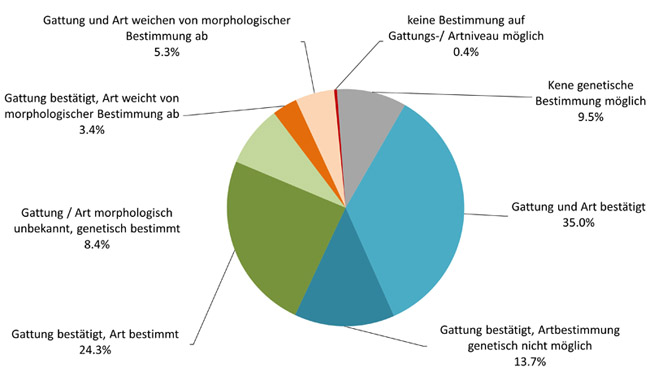
Im Rahmen der vom StMUV geförderten Projekte "Genetische Artbestimmung – ein Beitrag zur Qualitätssicherung in der biologischen Analytik von Oberflächengewässern" und „DNA-Barcoding – eine neue Möglichkeit für das Umweltmonitoring und den Gewässerschutz“ wurde geprüft, inwieweit DNA-Barcoding als Baustein der biologischen Qualitätssicherung bei der Artbestimmung von Makrozoobenthos geeignet ist. Dazu wurde die Methodik im Hinblick auf Konservierung des Probenmaterials, DNA-Extraktion und Vervielfältigung des Markergens COX1 (Cytochrom-c-Oxidase I) mit PCR optimiert und weiterentwickelt. Insgesamt konnten ca. 91 % der Makrozoobenthos-Proben genetisch identifiziert werden. Bei 5 % der Proben lieferte die Sequenzanalyse kein Ergebnis, da die Sequenz entweder nicht in der Datenbank enthalten (2 %) oder die Qualität zu schlecht war (z.B. Mischsequenz, 3 %). 4 % der Proben wurden nicht bestimmt, da das Markergen mit keiner der verwendeten Primerpaare vervielfältigt werden konnte. Während bei den Ephemeroptera (Eintagsfliegen), Plecoptera (Steinfliegen) und Coleoptera (Käfer) nahezu alle Proben genetisch bestimmbar waren, konnten bei den Trichoptera (Köcherfliegen) knapp 20 % und bei den Diptera (Zweiflügler) etwa 7 % der Organismen genetisch nicht identifiziert werden. Beim Vergleich der Ergebnisse der genetischen und der morphologischen Bestimmung kam es bei ca. 9 % der Proben zu Abweichungen. In diesen Fällen ist eine Plausibilitätsüberprüfung durch Taxonomie-Experten erforderlich.
Genetische Artbestimmung von Fledermäusen und Mäusen
Fledermäuse gelten allesamt als gefährdete Arten. Um sie zu schützen ist es wichtig, die Arten genau zu identifizieren und deren Verbreitung zu kennen. Aber wie kann man diese nachtaktiven Flieger bestimmen ohne sie zu fangen oder in ihren Quartieren zu stören? Das LfU setzte zur Artbestimmung eine nicht invasive Methode mittels DNA-Analyse aus Fledermaus-Kot ein, der in den Quartieren - z.B. unter Kirchendächern - leicht zugänglich ist. Im Kot befinden sich u.a. auch Zellen der Darmschleimhaut, die für die Analytik ausreichen. Für die Bestimmung der 24 einheimischen Fledermausarten wurden am LfU drei mitochondriale Gene verwendet: (1) die 12S-16S-rRNA, (2) eine Untereinheit der Cytochrom-c-Oxidase und (3) das Gen für die NADH-Dehydrogenase.
Mit Hilfe von DNA-Barcoding konnte auch ein Exemplar der viele Jahre verschollenen und im Herbst 2023 nach über 60 Jahren wiederentdeckten Bayerischen Kurzohrmaus (Microtus bavaricus) genetisch bestätigt werden.
Neobiota
Neue Tierarten, sogenannte „Neozoen“, die in unsere Gewässer einwandern und sich dort verbreiten sind gleichermaßen ein Problem der Wasserwirtschaft und des Naturschutzes. Sie greifen in das Nahrungsnetz ein, verdrängen oft die heimischen Arten und vermehren sich in der Regel sehr rasch, wenn natürliche Feinde fehlen. Vernetzte Gewässer, Schiffsverkehr und Boots-Tourismus bilden ideale Voraussetzungen für die unbewusste Ausbreitung fremder Arten. DNA-Untersuchungen können hier dazu beitragen, Identität, Herkunft und Verwandtschaftsbeziehungen zu klären.
Eine dieser invasiven Arten ist der Höckerflohkrebs Dikerogammarus villosus (Amphipoda). Er hat u.a. den Bodensee besiedelt und breitet sich dort aus. Ein Teilprojekt des LfU widmete sich diesem illegalen Einwanderer.
 Der Höckerflohkrebs Dikerogammarus villosus ist ein illegaler Einwanderer, der den Bodensee erobert; Foto: Martin Huber, Wasserwirtschaftsamt Kempten
Der Höckerflohkrebs Dikerogammarus villosus ist ein illegaler Einwanderer, der den Bodensee erobert; Foto: Martin Huber, Wasserwirtschaftsamt KemptenDer zu den Flohkrebsen (Amphipoda) gehörende Höckerflohkrebs Dikerogammarus villosus stammt aus dem Pontokaspischen Raum und ist vom Kaspischen Meer über die Donau in bayerische Gewässer gelangt. Die Tiere sind stark invasiv und verdrängen einheimische Arten, wie den kleineren Flussflohkrebs (Gammarus roeseli), aus ihrem angestammten Biotop.
Durch populationsgenetische Untersuchungen anhand von DNA-Tests sollte festgestellt werden, ob es sich um eine singuläre oder eine Mehrfacheinschleppung handelt und inwieweit Besiedlungsschübe genetisch manifestiert sind. Aus den Ergebnissen ließ sich ableiten, dass das Ufer des Bodensees mehrfach besiedelt wurde. Eine Besiedelung über den Rhein konnte nahezu ausgeschlossen werden. Die rasche Ausbreitung im See wurde vermutlich auch durch den regen Schiffsverkehr begünstigt.
Weiterführende Informationen
Links
- DNA-Barcoding – eine neue Möglichkeit für das Umweltmonitoring und den Gewässerschutz
- Genetische Artbestimmung – ein Beitrag zur Qualitätssicherung in der biologischen Analytik von Oberflächengewässern - PDF
- Genetische Verfahren im biologischen Monitoring - Vergleich klassisches Bestimmungsverfahren vs. genetisches Verfahren
- Eco-AlpsWater
- Artenhilfsprogramm Fledermäuse
- Bayerische Kurzohrmaus
- Wirbellose Neozoen im Bodensee - PDF